浙江万里学院再发Nature子刊:破解细菌基因“开关”密码的关键高精图谱
央广网宁波4月8日消息(记者俞烨 通讯员施冰洁)4月7日,浙江万里学院生物与环境学院夏亦荠教授与张海磊博士团队在国际知名期刊Nature Communications发表研究成果。团队成功构建细菌NAD+加帽RNA(NAD-RNA)的高精度鉴定体系,首次绘制出大肠杆菌NAD加帽RNA高分辨率图谱,为理解这一新型RNA修饰在基因表达与环境应激中的作用机制提供关键方法学支撑。浙江万里学院为论文第一完成单位,彰显地方应用型高校在基础科研领域的创新实力。

Nature子刊发表截图(央广网发 浙江万里学院供图)
“5'端加帽”: 一个让RNA“与众不同”的身份标签
这项研究听起来有些深奥,但背后的科学原理非常引人入胜。
在生命科学领域,所有生物体内都有一个“基因表达”的过程。如果把DNA比作一本“天书”,RNA就是抄录天书内容传递给细胞的“信使”。过去人们认为,原核生物(比如大肠杆菌)的RNA是不需要“加帽”的,这与真核生物(比如人类)的RNA有着本质区别。
然而,近年来科学家意外发现,细菌里居然也有类似真核生物“5'端帽子”的结构,这种“帽子”是一种叫做NAD+(烟酰胺腺嘌呤二核苷酸)的辅酶分子。NAD+不仅是人体中负责能量代谢和细胞修复的“生命引擎”,它在RNA上出现,暗示着RNA可能因此获得了一种全新的身份标识——不仅是信使,更是生命体在应对环境变化时的“智能开关”。
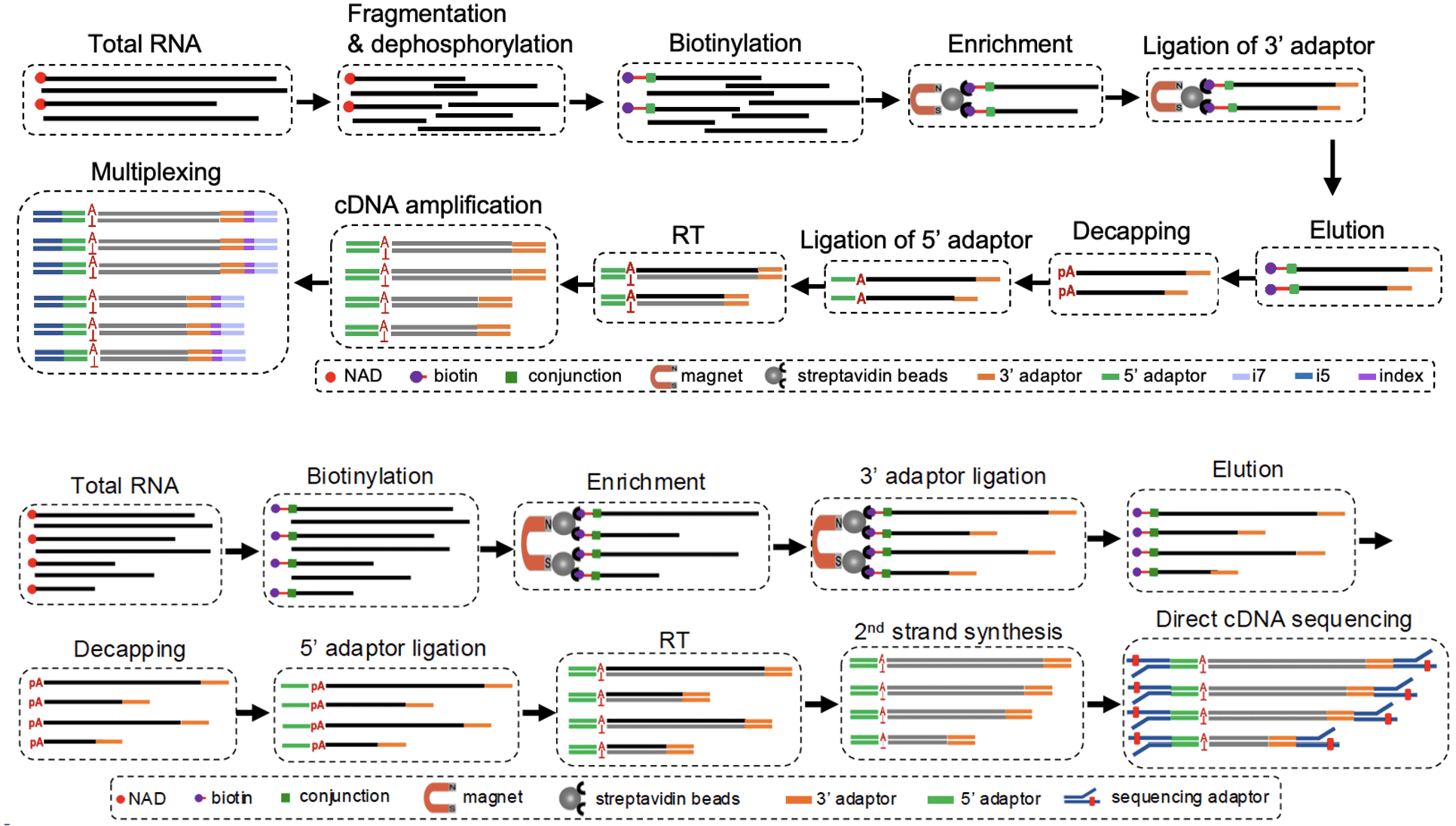
pNAD-seq(上)和NAD-linkSeq(下)流程图(央广网发 浙江万里学院供图)
技术破壁:万里团队发明“精准测序方法”
尽管NAD+加帽RNA的发现令人兴奋,但这一领域此前面临两大“拦路虎”:一是5'端定位精度不够,看不清楚帽子到底戴在哪里;二是短链RNA经常被遗漏,许多重要信息可能因此被忽视。
为了看清这顶“帽子”,万里学院团队下了一番“绣花”功夫。他们开发了两套互补的“分子追踪器”:一是pNAD-seq技术,通过独创的化学反应,像“捕虫网”一样精准捕获并精确定位带有NAD帽子的RNA;二是NAD-linkSeq技术,利用Nanopore测序平台,像“基因测序仪”一样完整读取这些RNA的全长序列。
这套组合拳不仅能精确找到RNA的起点,还极大提升了对短链RNA的“搜寻”能力,为这个新兴领域提供了一套可拓展至真核生物的高精度鉴定方案。
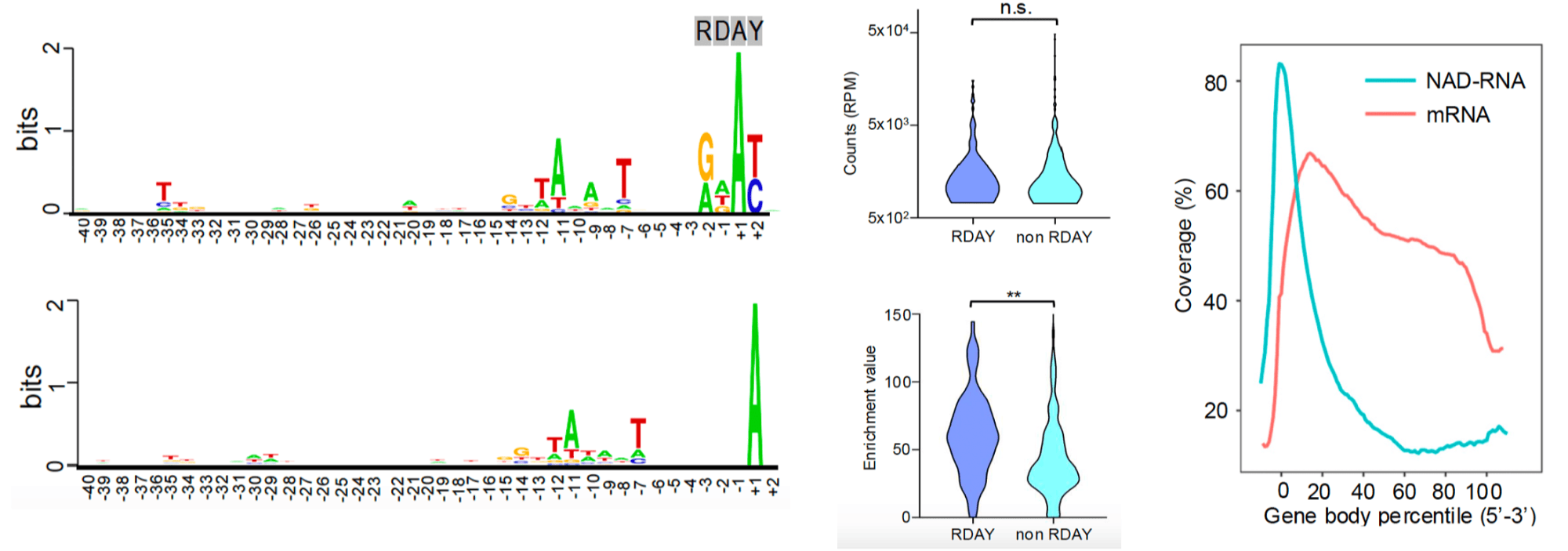
保守序列与转录本长度特征(央广网发 浙江万里学院供图)
发现规律:找到NAD 加帽的“暗号”
有了高精度的追踪工具,团队终于揭开了这顶“帽子”的神秘面纱。他们绘制出了迄今最完备的大肠杆菌NAD+加帽RNA全转录组高分辨率图谱。这个图谱就像一张“基因地图”,不仅标记出了哪些基因被加上了NAD“帽子”,更重要的是,发现了NAD加帽的规律——在转录起始位点附近,存在一个神秘的保守序列“RDAY” 。统计表明,携带这个序列的启动子通常会产生较高比例带NAD帽子的转录本。
这就像在茫茫的基因序列中,发现了一句“暗号”,科学家掌握了它,就可能在未来人为调控这些基因的“开关”。
更令人振奋的是,在氮源限制等胁迫环境下,NAD-RNA表现出显著的启动子切换现象,这意味着这些“帽子”很可能是细菌感知环境变化并迅速调整基因表达的关键调节器。
万里“顶刊现象”:从偶然到常态的科研生态
对于一所地方应用型高校来说,能够在《Science》和《Nature》系列顶级期刊上持续产出,实属不易。
2018年,钱国英、葛楚天教授团队与美国杜克大学合作,在《Science》上发表研究成果,揭开了龟类“温度依赖型性别决定”的神秘面纱,成为宁波地区首篇《Science》论文。
2020年,该团队再次登上《Science》,进一步揭示pSTAT3调控Kdm6b的分子机制,相关原创成果被编入国际经典生物学教科书《Developmental Biology》。2025年,团队研究成果又登Science Advances(《科学》子刊)。
2025年,该校碳中和研究院在《Nature Communications》发表CO2资源化利用研究成果,为工业碳减排提供了新思路。
从2018年实现《Science》“零的突破”,到如今在Nature子刊持续产出,浙江万里学院的“顶刊现象”已不再是偶然的孤例,而是形成了特色鲜明的科研生态。学校在动物生殖发育、碳中和与环境工程、生物医药与大健康等交叉领域持续发力,从“万里现象”到“万里实力”,学校以应用型大学定位撬动基础研究突破,生动诠释“小学校也能做大学问”的科研韧性。
